RNA polimerasi
In biochimica l'RNA polimerasi è un enzima appartenente alla classe delle transferasi, che catalizza la seguente reazione:
| RNA polimerasi (DNA-dipendente) | |
|---|---|
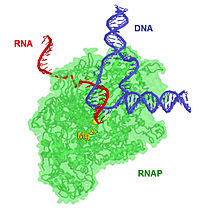 RNA Polimerasi di T.Aquaticus rappresentata durante l'elongazione di un trascritto primario in direzione 5'->3'. Lo ione magnesio Mg2+ (in giallo) è localizzato nel sito attivo dell'enzima e complessa l'ossidrile 3' del ribonucleotide terminale per favorire l'attacco nucleofilo dell'ossigeno sul fosfato alfa del nucleoside trifosfato entrante. | |
| Numero EC | 2.7.7.6 |
| Classe | Transferasi |
| Nome sistematico | |
| nucleoside-trifosfato:RNA nucleotidiltransferasi (DNA-dipendente) | |
| Altri nomi | |
| RNA polimerasi; RNA polimerasi I; RNA polimerasi II; RNA polimerasi III; nucleotidiltransferasi DNA-dipendente; RNA trascrittasi; trascrittasi | |
| Banche dati | BRENDA, EXPASY, GTD, PDB (RCSB PDB PDBe PDBj PDBsum) |
| Fonte: IUBMB | |
- nucleotide trifosfato + RNAn ⇄ pirofosfato + RNAn+1
Con questa reazione l'enzima catalizza la sintesi di un filamento di RNA. Generalmente con il nome RNA polimerasi si identifica la RNA polimerasi-DNA dipendente che, nel processo denominato trascrizione, sintetizza un filamento di RNA complementare ad uno stampo di DNA. Esistono anche RNA polimerasi-RNA dipendenti, coinvolte nel processo di replicazione del genoma di alcuni virus che possiedono un genoma ad RNA.
L'attività di sintesi della RNA polimerasi necessita dei quattro ribonucleosidi-trifosfati che entreranno a far parte della molecola di RNA (ATP, GTP, CTP e UTP) e ioni metallici (Mn2+ e Mg2+).
Azione dell'RNA polimerasi
modificaInizio
modificaIl legame dell'RNA polimerasi, nei procarioti, comporta che la subunità α riconosca l'elemento a monte (da 40 a -70 pb) nel DNA, così come il fattore σ va a riconoscere la regione da -10 a -35 (le TATA box). Ci sono molti fattori σ che regolano l'espressione genica. Per esempio, σ70 è espresso in condizioni normali e permette che l'RNA polimerasi vada a legarsi ai geni house-keeping, mentre σ32 determina il legame dell'RNA polimerasi con i geni heat-shock. Dopo il legame col DNA, l'RNA polimerasi passa da un complesso chiuso ad un complesso aperto. Tale cambiamento comporta la separazione dei filamenti di DNA per andare a formare una parte di DNA srotolato di circa 13 bp. I ribonucleotidi sono legati alle basi del filamento stampo di DNA. Davanti alla RNA polimerasi il DNA si svolge, mentre i filamenti che la polimerasi stessa si lascia dietro, si riavvolgono.
Allungamento
modificaTale fase comporta l'ulteriore aggiunta di ribonucleotidi e il cambiamento del complesso aperto a complesso di trascrizione. L'RNA polimerasi non può iniziare a formare trascritti troppo lunghi a causa del suo stretto legame al promotore. In questa fase iniziale si ottengono corti frammenti di RNA di circa 9 bp attraverso un processo detto trascrizione abortiva. Una volta che l'RNA polimerasi inizia a formare trascritti più lunghi, il fattore σ si stacca dal promotore. Durante la fase di allungamento il fattore σ perde affinità con il core enzimatico e si distacca da esso per impiegare un nuovo legame con un'altra RNA polimerasi. Il complesso trascrizionale di 17 bp ha un ibrido DNA-RNA di 8 bp, cioè 8 coppie di basi implicano che il trascritto di RNA si leghi allo stampo di DNA. Come la trascrizione va avanti, vengono aggiunti ribonucleotidi al 3' terminale del trascritto di RNA e il complesso di RNAP si muove lungo il DNA. L'aggiunta di ribonucleotidi al trascritto di RNA è un meccanismo molto simile alla polimerizzazione del DNA e si ritiene che queste due polimerasi siano evolutivamente correlate.
Terminazione
modificaÈ segnalata da elementi di controllo detti "sequenze di terminazione" o terminatori. Possiamo avere terminatori Rho-dipendenti e Rho-indipendenti. I Rho-indipendenti sono costituiti da una sequenza con simmetria bipartita: la RNA polimerasi trascrive la sequenza di terminazione che, dato che presenta questa simmetria bipartita, si ripiega a formare una forcina; si suppone che questa struttura a forcina causi terminazione perché impedisce la progressione della polimerasi. I Rho-dipendenti non hanno la catena AT tipica dei terminatori Rho-indipendenti e molti di essi non formano strutture a forcina; il fattore Rho, in questo caso, ha un dominio di legame all'RNA e un dominio ATPasico. Il fattore Rho si lega alla sequenza terminatore sull'RNA sintetizzata dall'RNA polimerasi. Una volta legato, Rho con l'attività ATPasica idrolizza ATP e usa questa energia per separare l'RNA dall'RNA polimerasi e dallo stampo a DNA.
RNA polimerasi eubatteriche
modificaNegli eubatteri è presente una sola RNA polimerasi, coinvolta nel processo di trascrizione dei geni. Essa si associa di volta in volta a diverse subunità σ che le permettono la localizzazione a livello dei promotori di specifici gruppi di geni. Ovviamente, rientrano tra queste RNA polimerasi anche quelle degli eubatteri endosimbionti miticondriale e plastidiale, in genere erroneamente ascritte tra le RNA eucariotiche.
RNA polimerasi archeobatteriche ed eucariotiche
modificaSeparato dagli eubatteri è il ramo che ha portato agli attuali archei ed eucarioti, che sono strettamente imparentati.
Negli eucarioti sono presenti tre diverse RNA polimerasi principali. Tutte le polimerasi sono eteropolimeri costituiti da molte subunità differenti, che, singolarmente o in diverse combinazioni, catalizzano le fasi di inizio, di allungamento e terminazione della sintesi del polimero. Le tre polimerasi eucariotiche differiscono sia per la struttura che per la funzione dell'RNA neosintetizzato: la polimerasi-1 presiede alla sintesi degli RNA-ribosomiali, la 2 catalizza la sintesi degli RNA-messaggeri, la 3 catalizza la sintesi degli RNA di trasferimento e dei piccoli RNA-ribosomiali. Tali polimerasi sono costituite da più di 10 subunità con funzioni diverse. Il complesso di trascrizione risulta così formato, oltre che dalla polimerasi e dal DNA-stampo, anche da molti fattori proteici di trascrizione che hanno la funzione di presiedere al riconoscimento della sequenza di inizio e delle fasi successive della polimerizzazione, oltre che quella di mediare e integrare i messaggi di repressione e derepressione della fase di trascrizione.
| Enzima | Geni trascritti |
| RNA polimerasi I | Geni per RNA ribosomiali 28S, 5.8S e 18S (geni non codificanti per proteine) |
| RNA polimerasi II | Geni codificanti proteine (mRNA), geni per la maggior parte dei piccoli RNA nucleari e nucleolari (snRNA e snoRNA), geni per microRNA e RNA delle telomerasi |
| RNA polimerasi III | Geni per RNA transfer, RNA ribosomiali 5S, alcuni piccoli RNA nucleari (ad esempio snRNA U6) e piccoli RNA citoplasmatici (scRNA) (geni non codificanti) |
A queste 3 se ne aggiungono altre 2:
la IV, caratterizzata dal fatto di non essere sempre attiva. Protegge la cellula dalla α-Amanitina (la tossina dell'Amanita falloide), continuando a produrre mRNA;
la V, che con la precedente sintetizza i siRNA nelle piante.
Le RNA polimerasi archeobatteriche sono di un solo tipo, ma sono molto simili a quelle dei loro stretti cugini eucarioti. Questi hanno la RNA polimerasi II composta da 12 subunità; la RNA polimerasi archeobatterica è un complesso simile, con 11 o più subunità. Anche le sequenze amminoacidiche tra le due RNA polimerasi è molto simile. Inoltre i promotori degli archeobatteri hanno una sequenza complesso molto simile al TATA box dei promotori eucariotici, con funzione analoga.
Ci sono, poi, le RNA polimerasi "mitocondriale" e "plastidiale", cioè dell'alfa-proteobatterio e del cianobatterio endosimbionti, che sono, quindi, eubatteriche, anche se vengono generalmente ascritte, erroneamente tra le polimerasi eucariotiche.
Bibliografia
modifica- Krakow, J.S. e Ochoa, S. RNA polymerase from Azotobacter vinelandii. Methods Enzymol. 6 (1963) 11–17.
- Mans, R.J. e Walter, T.J. Transfer RNA-primed oligoadenylate synthesis in maize seedlings. II. Primer, substrate and metal specificities and size of product. Biochim. Biophys. Acta 247 (1971) 113–121. Entrez PubMed 4946277
- Roeder, R.G. In: Losick, R. e Chamberlin, M. (Eds), RNA Polymerase. Cold Spring Harbor Laboratory, 1976, p. 285.
- Sheldon, R., Jurale, C. e Kates, J. Detection of polyadenylic acid sequences in viral and eukaryotic RNA(poly(U)-cellulose columns-poly(U) filters-fiberglass-HeLa cells-bacteriophage T4). Proc. Natl. Acad. Sci. USA 69 (1972) 417–421. Entrez PubMed 4501121
- Weaver, R.F., Blatti, S.P. e Rutter, W.J. Molecular structures of DNA-dependent RNA polymerases (II) from calf thymus and rat liver. Proc. Natl. Acad. Sci. USA 68 (1971) 2994–2999. Entrez PubMed 5289245
Voci correlate
modificaAltri progetti
modifica- Wikimedia Commons contiene immagini o altri file su RNA polimerasi
Collegamenti esterni
modifica- Loredana Verdone, RNA polimerasi, in Enciclopedia della scienza e della tecnica, Istituto dell'Enciclopedia Italiana, 2007-2008.
- (EN) RNA polymerase, su Enciclopedia Britannica, Encyclopædia Britannica, Inc.
| Controllo di autorità | LCCN (EN) sh87001690 · J9U (EN, HE) 987007541391605171 · NDL (EN, JA) 00575477 |
|---|